Os pesquisadores aliaram tecnologia de ponta a uma técnica centenária para estudar as pequeninas células.
Nem seria preciso comentar o quão importante é ter a capacidade de ver os neurônios e suas conexões de dentro do cérebro, o quanto isso pode ajudar a entender o próprio funcionamento deste órgão quando saudável e também quando doente. Não surpreendentemente, essa é uma questão que desafia neurocientistas há bastante tempo!
No final do século XIX, o italiano Camillo Golgi criou uma técnica revolucionária que permite corar células no cérebro com uso de um precipitado de prata. Curiosamente, apenas cerca de 1-3% dos neurônios totais são corados dessa forma, o que facilita a vizualização de seus limites e formato com clareza. Esse feito rendeu-lhe o prêmio Nobel de fisiologia em 1906, divido com o espanhol Santiago Ramón y Cajal, seu grande rival. Usando a mesma técnica de coloração desenvolvida por Golgi, Ramón y Cajal demonstrou que o cérebro é formado por células individualizadas “contíguas” – próximas, conectadas, porém não-contínuas, como acreditava Golgi. A teoria de Ramón y Cajal ficou conhecida como doutrina neuronal do sistema nervoso, tendo sido muitas vezes posta à prova e comprovada ao longo destes anos.
De volta ao século XXI, enxergar os neurônios ainda não é uma tarefa fácil, principalmente as conexões entre eles. As técnicas tradicionais de microscopia óptica, que permitem sua visualização em detalhe, envolvem o corte do cérebro em fatias muito finas e, com isso, perde-se muita informação sobre como um neurônio conecta-se com outro. Outro tipo de técnica frequentemente utilizada é o imageamento por ressonância magnética, nesse caso, pode-se obter imagens em 3D do cérebro intacto e suas conexões neurais ativas em tempo real, porém, com pouca resolução para estudo a um nível celular.
Nesse contexto, pesquisadores brasileiros buscaram aplicar uma técnica chamada microtomografia computadorizada de raio-X. Os raios-X são produzidos por um acelerador de partículas, um “síncroton”. Como isso funciona? Quando um elétron (partícula muito pequena com carga negativa) está se movendo e troca de direção, ele emite energia. Quando esse movimento é rápido o suficiente, a energia liberada é no comprimento de onda do raio-X. Por meio de campos eletromagnéticos (criados por pequenos ímãs), o acelerador de partículas acelera os elétrons em órbitas circulares de forma sincronizada e, periodicamente, os muda de direção. O nome síncroton vem desta ação sincronizada do acelerador. A luz síncroton, nesse caso, feixes de raio-X, são capazes de penetrar a matéria, revelando seus detalhes em alta resolução. Mas como?
Quando você bate uma chapa de raio-X, por exemplo, os raios atravessam seu corpo e são absorvidos diferentemente pelos tecidos que possuem diferentes densidades, o resultado é uma “fotografia” do outro lado que contrasta os tecidos de maior e menor absorção em 2D. Na tomografia, no entanto, um scanner passa muitas vezes ao redor do corpo, resultando em imagens de muitos ângulos diferentes. Essas imagens são utilizadas para formar camadas bidimensionais, como fatias do corpo, que quando unidas no computador, permitem a visualização de estruturas em 3D.
Entretanto, nos tecidos moles, como o cérebro, a diferença na absorção dos raios-X é muito pequena, resultando em pouco contraste. Nesse caso, um método eficiente para se obter imagens com alto constraste é baseado nas mudanças de direção do feixe de ondas do raio-X conforme ele atravessa o tecido. Esse método é chamado de contraste de fase baseado na propagação de raio-X e tem sido utilizado para estudo do cérebro a nível celular. Porém, por conta da grande quantidade de neurônios em algumas regiões cerebrais, ainda sim, torna-se difícil diferenciar os prolongamentos de um e de outro, e estudá-los de forma individualizada. Uma alternativa a estas metodologias, é aumentar o contraste da imagem do raio-X por impregnar a amostra com um composto químico que o absorva; e assim, voltamos a técnica de Golgi.
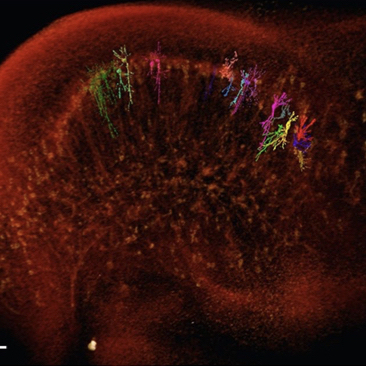
No trabalho recém-publicado na revista científica Scientific Reports, o grupo paulista de pesquisadores liderado pelo Dr. Matheus de Castro Fonseca, atrelou a microtomografia computadorizada de raios-X com uma adaptação da coloração de Golgi, utilizando o mercúrio ao invés da prata (Golgi-Cox). Dessa forma, obtiveram lindas imagens de neurônios individualizados do córtex e hipocampo intactos de camundongos. Nessas imagens, pode-se observar todos os prolongamentos (axônios e dendritos) e corpo celular dessas células com alta definição e aumento, tudo em 3D! Pode-se também investigar a conexão entre neurônios em diferentes áreas cerebrais com grande precisão. A técnica relatada no estudo poderia ser utilizada para comparar a arquitetura de um cérebro saudável com um doente, como na doença de Alzheimer ou de Parkinson, por exemplo.
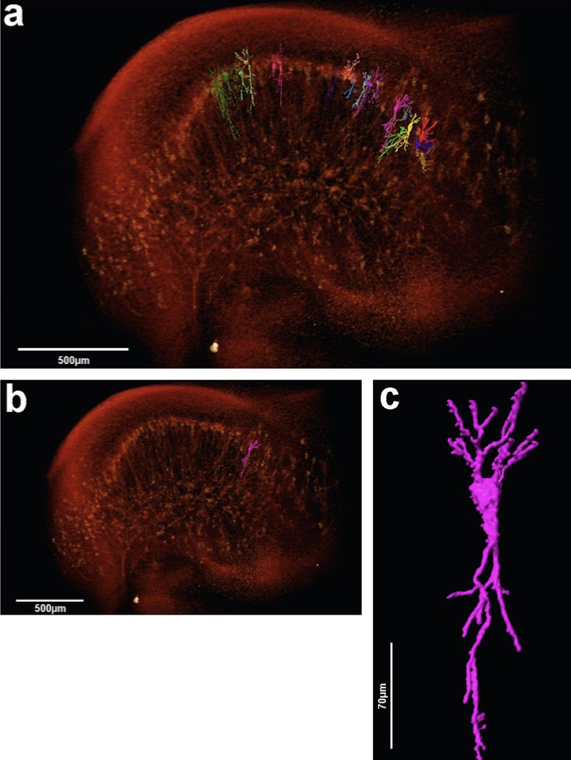
Nessa figura, Fonseca et al. mostram a separação de células com a técnica desenvolvida. Na foto (a) vê-se diferentes neurônios individualizados (diferentes cores) no hipocampo de camundongos. Na foto (b) destaca-se um único neurônio, visto em maior aumento e grande detalhamento na foto (c). (Adaptado de Fonseca et al., Sci. Reports, 2018).
Fonte: Fonseca et al., Scientific Reports (2018) 8:12074. DOI:10.1038/s41598-018-30501-x.